シーケンスアセンブリソフトウェア ATGC は大量のフラグメントの結合処理を高速に行い、波形の信頼度を考慮してコンセンサス配列の決定をするソフトウェアです。
次世代シーケンサーのデータにも対応しており、ゲノムマッピング、De novo Assembly 等の解析をご利用いただけます。
次世代シーケンサー対応機能 (64bit OS のみ)
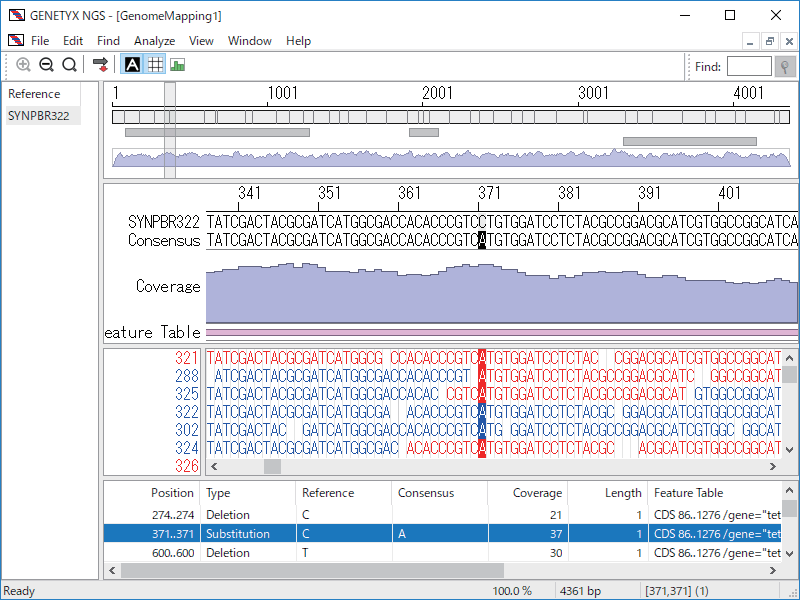
ゲノムマッピング
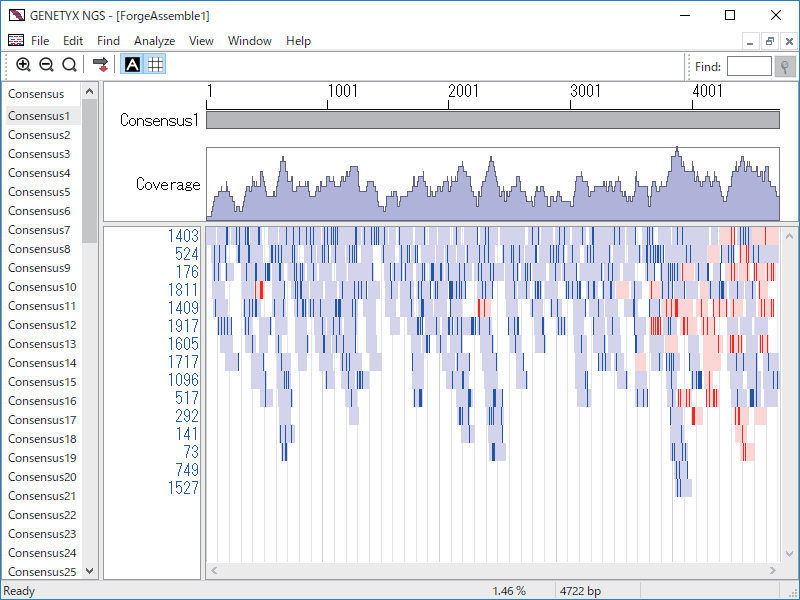
アセンブリ
- ゲノムマッピング
次世代シーケンサーからの断片配列 (FASTA、FASTQ、FNA/QUAL、CSFASTA) を既知のゲノム配列 (参照配列) にマッピングします。
- SAM / BAM インポート
マッピング等の解析で一般的に使われる SAM / BAM 形式のファイルを読み込んで、ゲノムマッピングの結果と同時に表示します。
- 変異表
ゲノムマッピングによって得られたコンセンサス配列と参照配列を比較して、その変異を一覧表示します。変異表は印刷や CSV 形式でのファイルで出力できます。
- de novo Assembly ●
Forge・MIRA▲ を使用して、次世代シーケンサーから出力された断片配列の de novo Assembly を行います。
- クオリティチェック機能
マッピングやアセンブルなどの解析を行う前にシーケンサーから出力された配列の質 (クオリティスコア、塩基組成、配列長、重複など) を調査します。
- トリミング機能
入力した配列に対してアダプター配列や低クオリティ領域を切り取るトリミング処理を行い新しいファイルに出力します。
- 配列組成表示機能
任意の範囲を指定してマッピングされた配列の組成を計算して出力します。
- 配列全体 MAP 表示機能 ●
配列全体の MAP を表示します。
- 解析履歴機能 ●
過去に行った解析の結果と条件を表示できます。
- 発現量解析機能 (カウントのみ) ●▲
マッピングの結果を元に発現量解析 (現在はカウント機能のみ) を行います。
シーケンサー出力のアセンブル
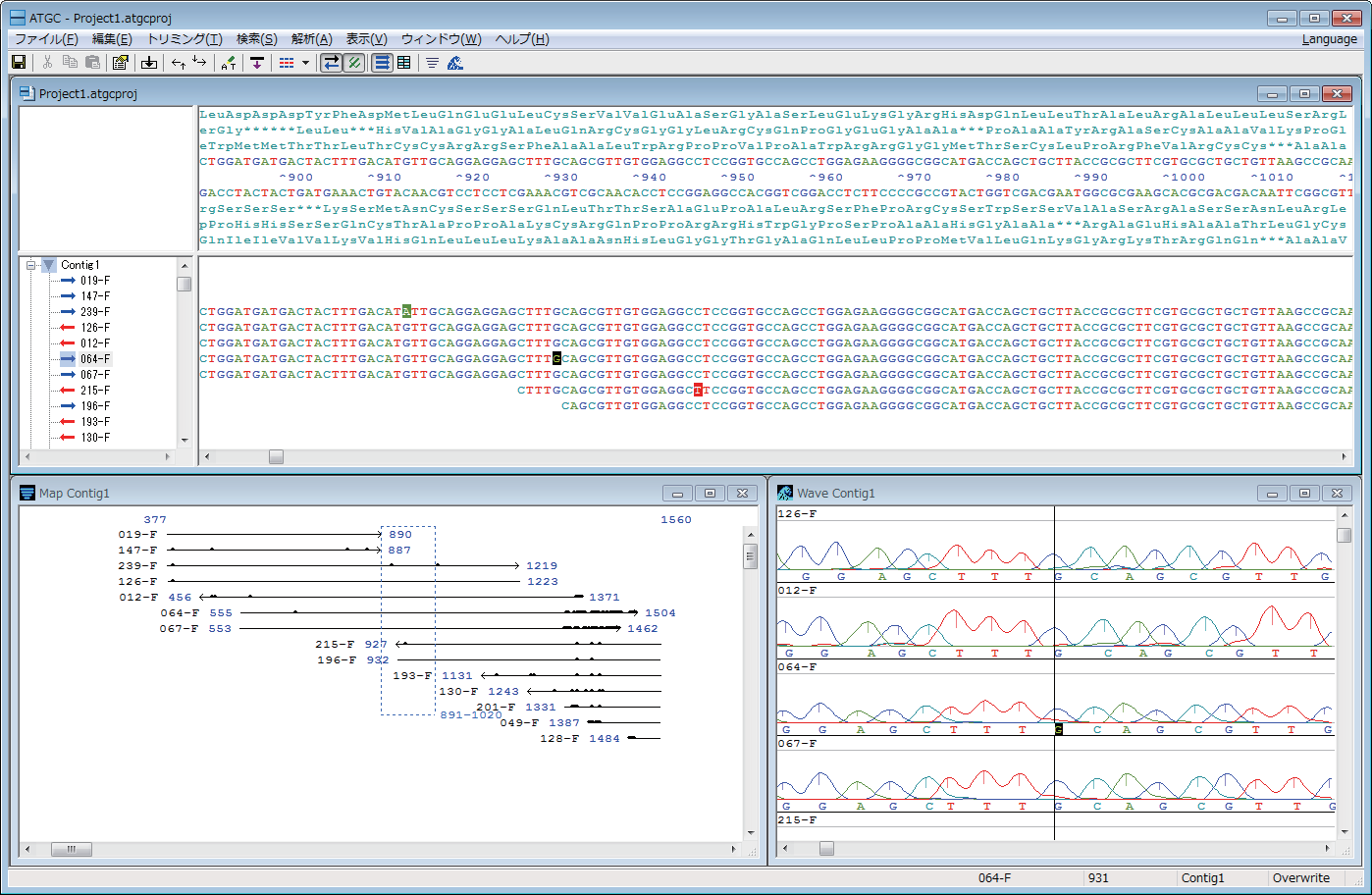
編集画面・結合マップ・波形表示の連動
- 編集画面・結合マップ・波形表示の連動
編集画面に連動して結合マップと波形表示がスクロールするので、波形を確認しながらの編集作業が効率よく行えます。
- コンティグ全体の波形印刷
アライメントした状態での断片配列の波形データをコンティグ全体にわたって印刷できます。
- 比較要約表示
コンセンサス配列と断片配列が異なる部分だけを要約して表示します。波形表示と連動するのでベースコールを素早く評価できます。
- ベクター配列のトリミング
ベクター配列を検索して、断片配列を読み込む際にその部分を取り除きます。目的の塩基配列のみをアセンブルすることができます。
- アミノ酸翻訳表示
コンセンサス配列からアミノ酸へ翻訳して、コンセンサス配列と同時に表示できます。
- ブロック表示
コンティグを先頭から一定間隔 (3bp, 10bp 等) ごとに空白で区切りブロック表示することができます。
●印は Ver.9 で新規追加された機能です。
▲印は別途ダウンロードが必要です。
動作環境
| 対応機種 | Microsoft Windows 10 / 8.1 / 7 が動作する機種 |
|---|---|
| 対応 OS | Microsoft Windows 10 / 8.1 / 7 日本語版 32bit OS / 64bit OS ※次世代シーケンサー対応機能は 64bit OS のみ |
| メモリ | 2GB 以上 (推奨 4GB 以上) |
| ストレージ容量 | 1GB 以上の空き容量 |
| ハードウェア | 光学ドライブ (インストール時に利用します。) |
| その他 | Internet Explorer Ver.11 以上がインストールされていること。 |
| 本製品のご使用にはインターネットによるライセンス認証が必要 |
Copyright © NIHON SERVER CORPORATION All Rights Reserved.








